Dehydrogenaza NADH
Dehydrogenaza NADH (ubichinon)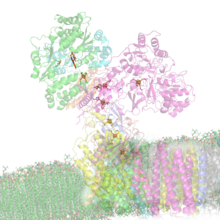 Struktura dehydrogenazy NADH z naciskiem na wewnątrzcząsteczkowe transportery elektronów ( PDB 2FUG ). Obserwujemy siedem wyrównane klastrów żelaza siarki umożliwiające przepływ elektronów z NADH w macierzy mitochondrialnej (u góry), poprzez na FMN kofaktor i ubichinon , w przeliczeniu na ubichinolu w wewnętrzną błonę mitochondrialną (na dole).
Struktura dehydrogenazy NADH z naciskiem na wewnątrzcząsteczkowe transportery elektronów ( PDB 2FUG ). Obserwujemy siedem wyrównane klastrów żelaza siarki umożliwiające przepływ elektronów z NADH w macierzy mitochondrialnej (u góry), poprzez na FMN kofaktor i ubichinon , w przeliczeniu na ubichinolu w wewnętrzną błonę mitochondrialną (na dole).
| Nr WE | WE |
|---|---|
| numer CAS | |
| Współtwórcy | FMN ; Fe-S |
| IUBMB | Wpis IUBMB |
|---|---|
| IntEnz | Widok IntEnz |
| BRENDA | Wejście BRENDA |
| KEGG | Wejście KEGG |
| MetaCyc | Szlak metaboliczny |
| PRIAM | Profil |
| PDB | Struktury |
| UDAĆ SIĘ | AmiGO / EGO |
Dehydrogenazy NADH lub złożony , że w łańcuchu oddechowym jest oksydoreduktaza membrana , która katalizuje się reakcję :
NADH + ubichinon + 5 H + matrix NAD + + ubichinol + 4 H + międzybłonowy .Ten enzym występuje w bardzo dużej liczbie żywych istot, od prokariotów do ludzi . Stanowi pierwszy punkt wejścia dla elektronów o wysokim potencjale przenoszenia do oddychania komórkowego i fosforylacji oksydacyjnej w mitochondriach oraz zapewnia transfer elektronów z NADH do koenzymu Q 10rozpuszczony w dwuwarstwie lipidowej . U eukariotów znajduje się w wewnętrznej błonie mitochondrialnej . Odegrałby również rolę w wyzwalaniu apoptozy ; ustalono korelację między aktywnością mitochondriów a apoptozą podczas rozwoju somatycznego zarodka .
Struktura i działanie
Kompleks I to największy i najbardziej skomplikowany enzym w łańcuchu oddechowym. U ssaków składa się z 44 łańcuchów polipeptydowych , z których siedem jest kodowanych przez genom mitochondrialny . Zawiera w szczególności grupę prostetyczną FMN i osiem klastrów żelazo-siarkowych , z których siedem jest zorientowanych tak, aby umożliwić cyrkulację elektronów od NADH do koenzymu Q 10. Przeniesienie tych elektronów z pary redoks, której standardowy potencjał wynosi -0,32 V, do pary redoks o standardowym potencjale 0,06 V uwalnia energię wystarczającą do aktywowania pompy protonowej, która wyrzuca cztery protony H + z macierzy mitochondrialnej do przestrzeni międzybłonowej przez wewnętrzną błona mitochondriów.
Ogólna struktura przyjmuje kształt litery L z długą domeną błonową składającą się z około sześćdziesięciu helis i obwodowej domeny hydrofilowej, w której znajdują się wszystkie centra redoks i miejsce wiązania NADH. Struktura kompleksu I eukariotów nie została jeszcze dobrze scharakteryzowana jako całość, ale ustalono strukturę domeny hydrofilowej bakterii Thermus thermophilus (en) ( PDB 2FUG ), a także domeny błonowej E. coli ( PDB 3RKO ) i T. thermophilus ( PDB 4HE8 ). Pełna struktura dehydrogenazy NADH T. thermophilus została po raz pierwszy opublikowana wluty 2013( WPB 4HEA ).
-
( fr ) Schemat funkcjonalny dehydrogenazy NADH przedstawiający jej ogólną postać składającą się z domeny hydrofilowej (dno) skąpanej w macierzy mitochondrialnej i oznaczonej siedmioma zrównanymi skupiskami żelazo-siarka kierującymi elektrony z macierzy NADH poprzez grupę protetyczną FMN do hydrofobowej domena (góra) zawarta w wewnętrznej błonie mitochondrialnej, w której znajduje się koenzym Q 10jest zredukowany w ubichinolu Q 10 H 2. Cztery protony H + są wyrzucane do mitochondrialnej przestrzeni międzybłonowej podczas tej reakcji, co pomaga wygenerować gradient stężenia protonów przez wewnętrzną błonę mitochondrialną.
Inhibitory
Rotenon jest inhibitorem Najbardziej znanym z kompleksu I . Jest powszechnie stosowany jako pestycyd i środek owadobójczy . Z izoflawonoidami (in) , rotenoidy są obecne w wielu rodzajach roślin tropikalnych, takich jak Antonia ( Loganiaceae ), Derris i Lonchocarpus ( Faboideae , Fabaceae ). Podobnie jak piericidin A (fr) , rotenonu wiąże się z miejscem wiązania na ubichinon o złożonej I .
Ryboza difosforan adenozyny (ADPR) jest inhibitorem dehydrogenazy NADH przez wiązanie się z miejscem wiązania nukleotydów, która blokuje wiązanie z NADH .
Rodzina acetogeniny jako najbardziej silnymi inhibitorami złożonego I . Cząsteczki te wiążą się z podjednostką ND2, co zwykle pokazuje, że ta ostatnia byłaby niezbędna do wiązania ubichinonu. Jedna z tych cząsteczek, rolliniastatyna-2, jest pierwszym inhibitorem kompleksu I , który nie wiąże się z tym samym miejscem co rotenon.
Metformina , przeciwcukrzycowe , jest również częściowe inhibitor kompleksu I , który wydaje się odgrywać kluczową rolę w jego sposobu działania.
Uwagi i odniesienia
- (in) Leonid A. Sazanov i Philip Hinchliffe , „ Struktura domeny hydrofilowej kompleksu oddechowego I z Thermus thermophilus ” , Science , vol. 311 n O 5766, 10 marca 2006, s. 1430-1436 ( PMID 16469879 , DOI 10.1126 / science.1123809 , Bibcode 2006Sci ... 311.1430S , czytaj online )
- (en) Eiko Nakamaru-Ogiso, Hongna Han, Akemi Matsuno-Yagi, Ehud Keinan, Subhash C. Sinha, Takao Yagi and Tomoko Ohnishi , „ Structure of the Hydrophilic Domain of Respiratory Complex I from Thermus thermophilus ” , FEBS Listy , t. 584, n O 5, 5 marca 2010, s. 883-888 ( PMID 20074573 , PMCID 2836797 , DOI 10.1016 / j.febslet.2010.01.004 , czytaj online )
- (w) Maria i Peter Chomova Racay , „ Kompleks mitochondrialny I w sieci znanych i nieznanych faktów ” , Fizjologia ogólna i biofizyka , tom. 29, n o 1, marzec 2010, s. 3-11 ( PMID 20371875 , DOI 10.4149 / gpb_2010_01_3 , czytaj online )
- (w) Elisa Petrussa Alberto Bertolini, Valentino Casolo Jana Krajňáková Francesco Macrì i Angelo Vianello , " Bioenergetyka mitochondrialna związana z manifestacją zaprogramowanej śmierci komórki Podczas embriogenezy somatycznej Abies alba " , Planta , t. 231 n o 1, grudzień 2009, s. 93-107 ( PMID 19834734 , DOI 10.1007 / s00425-009-1028-x , czytaj online )
- (w) Ulrich Brandt , " NADH przekształcający energię: oksydoreduktaza chinonowa (kompleks I) " , Annual Review of Biochemistry , vol. 75, lipiec 2006, s. 69-92 ( PMID 16756485 , DOI 10.1146 / annurev.biochem.75.103004.142539 , czytaj online )
- (w) Joe Carroll, Ian M. Fearnley, J. Mark Skehel1 Richard J. Shannon, Judy Hirst i John E. Walker2 , „ Bovine Complex I is a Complex of 45 Different Subunits ” , Journal of Biological Chemistry , vol. 281 n O 43 27 października 2006, s. 32724-32727 ( PMID 16950771 , DOI 10.1074 / jbc.M607135200 , czytaj online )
- (w) Eduardo Balsa Ricardo Marco, Ester-Perales Clemente, Radek Szklarczyk Enrique Calvo, Manuel O. Landázuri i José Antonio Enríquez , „ NDUFA4 Is a Complex Subunit of Mammalian IV of the Electron Transport Chain ” , Cell Metabolism , vol. 16 N O 3, 05 września 2012, s. 378-386 ( PMID 22902835 , DOI 10.1016 / j.cmet.2012.07.015 , czytaj online )
- (w) Rozbeh Baradaran, John M. Berrisford, Gurdeep S. Minhas i Leonid A. Sazanov , " Struktura krystaliczna całego kompleksu oddechowego I " , Nature , vol. 494, n O 7438, 28 lutego 2013, s. 443-448 ( PMID 23417064 , PMCID 3672946 , DOI 10.1038 / nature11871 , Bibcode 2013Natur.494..443B , czytaj online )
- (w) Tatyana V. Zharova i Andrei D. Vinogradov , „ Konkurencyjne hamowanie mitochondrialnej oksydoreduktazy NADH-ubichinonu (kompleks I) przez ADP-rybozę ” , Biochimica et Biophysica Acta (BBA) - Bioenergetics , vol. 1320 n O 3, 4 lipca 1997, s. 256-264 ( PMID 9230920 , DOI 10.1016 / S0005-2728 (97) 00029-7 , czytaj online )
- (w) Pan Degli Esposti, A. Ghelli Pan Ratta, D. i E. Cortes Estornell , „ Substancje naturalne (acetogeniny) z rodziny Annonaceae są silnymi inhibitorami mitochondrialnej dehydrogenazy NADH (kompleks I) ” , Biochemical Journal , tom . 301 n o 1, Lipiec 1994, s. 161-167 ( PMID 8037664 , PMCID 1137156 , DOI 10.1042 / bj3010161 , czytaj online )
- (w) Benoit Viollet Bruno Guigas, Nieves Garcia Sanz, Jocelyne Leclerc, Marc Foretz i Fabrizio Andreelli , „ Komórkowe i molekularne mechanizmy metforminy: przegląd ” , Clinical Science , vol. 122 N O 6, marzec 2012, s. 253-270 ( PMID 22117616 , PMCID 3398862 , DOI 10.1042 / CS20110386 , czytaj online )
